 1. 自噬通路在“指标库”里的定位
1. 自噬通路在“指标库”里的定位在你已经写过的 PI3K/AKT–mTOR、AMP-activated protein kinase(AMPK)等代谢与生长因子通路基础上, 宏自噬(macroautophagy,本文简称“自噬”)更像是细胞在能量与损伤压力下的“回收系统”: 通过 ULK1–Beclin 1–ATG 蛋白模块,形成双膜自噬小体,包裹受损蛋白、线粒体或其他细胞器,并与溶酶体融合完成降解。[1,2]
上游抑制常来自 mechanistic target of rapamycin complex 1(mTORC1),上游激活常来自 AMPK 等能量感应轴; 但本篇不再详细展开上游信号,而是聚焦:自噬本身要测哪些指标?各自代表什么?在什么实验平台上最好用?
快速印象: 可以把自噬的 readout 粗暴拆成三段: 启动(ULK1 等)→ 自噬小体形成(Beclin 1、ATG5–ATG12、LC3)→ 通量与降解(LC3-II、p62、溶酶体)。 所有实验最后都要回到一个词:flux(自噬通量,而不是“LC3-II 有没有变高”)。[1,2]
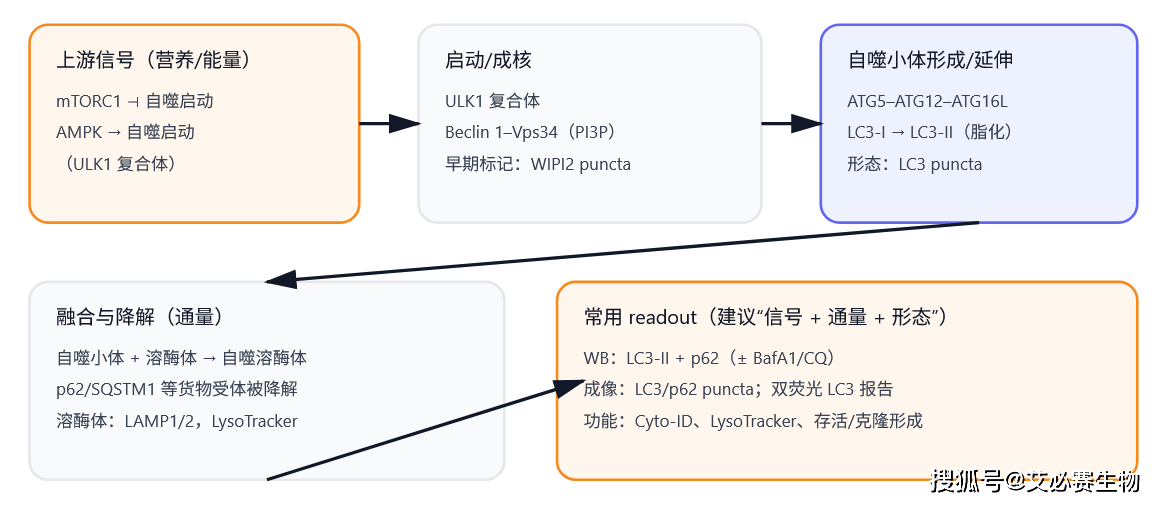 图1. 自噬通路“模块化读法”
图1. 自噬通路“模块化读法”
上游(mTORC1/AMPK)→ 启动/成核(ULK1、Beclin 1–Vps34)→ 形成(LC3 脂化)→ 融合与降解(通量、p62、溶酶体)。[1,2]
2. 一眼看懂:自噬通路核心 readout 列表
绝大多数自噬相关实验,最后都会落到一个问题:是自噬被激活了,还是被堵住了? 因此 panel 设计建议围绕有无降解端抑制剂 + LC3-II + p62 + 形态学证据来组合,而不是只看一条 LC3-II 条带。[1]
3.1 Panel A:饥饿 / mTOR 抑制诱导自噬
- 推荐组合:(可选)p-ULK1 + LC3-I/II + p62 ± 溶酶体标记(LAMP1/LysoTracker)
- 适用问题:自噬是否被拉起?不同细胞系/条件强度如何?
- 读图习惯:LC3-II 上升、p62 下降;加降解端抑制剂后 LC3-II 进一步累积更支持“通量确实增加”。[1,2]
3.2 Panel B:自噬通量评估(建议必做“± 抑制剂”)
- 推荐组合:LC3-I/II + p62 在 ± 抑制剂条件下的变化;(如有)双荧光 LC3 报告
- 适用问题:候选药物/基因操作是促进通量,还是堵在融合/降解端?
- 读图习惯:药物 + 抑制剂组 LC3-II 进一步累积:更支持“通量提升”。
- 药物本身让 LC3-II 很高且 p62 也高,加抑制剂变化不大:多提示“降解端堵车/溶酶体问题”。[1]
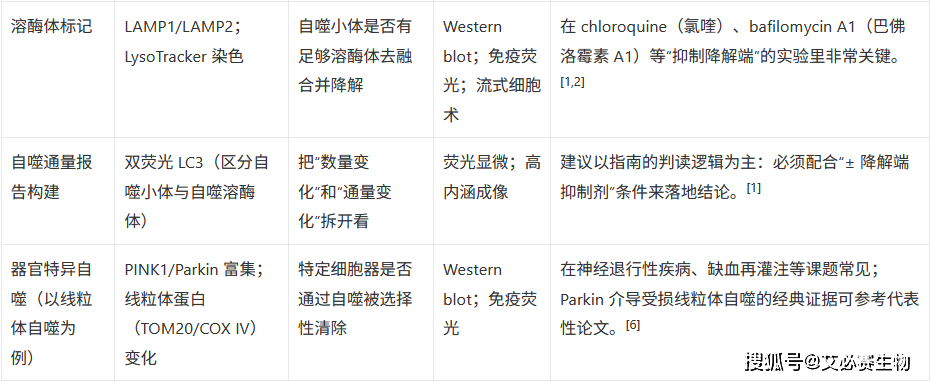
3.3 Panel C:器官特异自噬(以线粒体自噬为例)
- 推荐组合:LC3-II + p62 + PINK1/Parkin + 线粒体蛋白(TOM20、COX IV)
- 适用问题:应激是否通过线粒体自噬清除受损线粒体?
- 读图习惯:Parkin 富集、LC3 与线粒体共定位增加,随后线粒体蛋白整体下降。[6]
3.4 Panel D:自噬抑制剂 / 基因敲除验证
- 推荐组合:LC3-II + p62 ± 抑制剂 + 自噬核心基因(ATG5/ATG7/Beclin 1)干预
- 适用问题:候选表型是否真的是自噬依赖?
- 读图习惯:核心 ATG 缺失后,LC3-II 形成/通量读数与表型出现一致性“逆转/消失”。[1,2]
 图2. 自噬通量(flux)最常用的“落地判读”:把 LC3-II 与 p62 放进 “± 降解端抑制剂”框架中看
图2. 自噬通量(flux)最常用的“落地判读”:把 LC3-II 与 p62 放进 “± 降解端抑制剂”框架中看
把 LC3-II 与 p62 放进“± 降解端抑制剂(例如 bafilomycin A1、chloroquine)”框架中看,优先避免单指标误判。[1,2]

如果只想用最少的指标覆盖自噬通路,建议优先考虑:
- LC3-I/II:作为自噬小体形成的分子 readout。[1,4]
- p62/SQSTM1:作为货物降解与通量的反向 readout。[1,5]
- ± 降解端抑制剂条件:区分“生成多了”还是“堵在降解端”,这是 flux 判断关键。[1,2]
- 一个形态/功能 readout:例如 LC3/p62 puncta、双荧光 LC3、Cyto-ID 或 LysoTracker,帮助讲清“细胞里到底发生了什么”。[1]
加上本篇,你的信号通路指标库在“代谢–应激–命运”模块又补上了一个重要拼图:自噬。 后续在专题页中,我们将继续分享 PI3K/AKT–mTOR、AMPK、自噬、凋亡几篇串成一条“能量感应–自噬–生死决策”的路线。[1,2]
参考文献- Klionsky DJ, Abdel-Aziz AK, et al. Guidelines for the use and interpretation of assays for monitoring autophagy (3rd edition). Autophagy. 2016. doi:10.1080/15548627.2015.1100356.
- Mizushima N, Yoshimori T, Levine B. Methods in mammalian autophagy research. Cell. 2010. doi:10.1016/j.cell.2010.01.028.
- Kim J, Kundu M, Viollet B, Guan KL. AMPK and mTOR regulate autophagy through direct phosphorylation of Ulk1. Nature Cell Biology. 2011. doi:10.1038/ncb2152. :contentReference[oaicite:0]{index=0}
- Kabeya Y, Mizushima N, Ueno T, et al. LC3, a mammalian homologue of yeast Atg8, is localized in autophagosome membranes after processing. The EMBO Journal. 2000. doi:10.1093/emboj/19.21.5720. :contentReference[oaicite:1]{index=1}
- Pankiv S, Clausen TH, Lamark T, et al. p62/SQSTM1 binds directly to Atg8/LC3 to facilitate degradation of ubiquitinated protein aggregates by autophagy. Journal of Biological Chemistry. 2007. doi:10.1074/jbc.M702824200. :contentReference[oaicite:2]{index=2}
- Narendra D, Tanaka A, Suen DF, Youle RJ. Parkin is recruited selectively to impaired mitochondria and promotes their autophagy. Journal of Cell Biology. 2008. doi:10.1083/jcb.200809125.
)
)

)
)
)
)
)
)
)
)
)
)
)
)
)